几十年来,计算化学一直面临准确性与速度之间的拔河。密度泛函理论 (DFT) 等 Ab initio 方法提供高保真度,但计算成本高昂,将研究人员限制在只有几百个原子的系统上。相反,传统的力场速度很快,但通常缺乏复杂的键断裂或过渡态分析所需的化学准确性。
机器学习原子间相互作用势 (MLIP) 已成为以经典速度提供量子准确性的桥梁。但是,软件生态系统是一个新的瓶颈。虽然 MLIP 模型本身在 GPU 上运行,但周围的仿真基础设施通常依赖于以 CPU 为中心的传统代码。
NVIDIA ALCHEMI (化学和材料创新 AI 实验室) 通过利用 AI 加速化学和材料发现,帮助应对这些挑战。我们之前宣布了 ALCHEMI 产品组合的两个组成部分:
- ALCHEMI NIM 微服务: 适用于化学和材料科学领域 AI 加速批量原子模拟的可扩展、云就绪型微服务
- ALCHEMI 工具包 – Ops:一组基础 GPU 内核,旨在加速模拟背后的计算,例如近邻列表、色散校正和静电
今天,我们将推出 NVIDIA ALCHEMI Toolkit,这是一组 GPU 加速的模拟构建块,整合并扩展了 ALCHEMI Toolkit-Ops。ALCHEMI 工具包旨在管理加速化学和材质领域特定内核与深度学习模型之间的数据流。ALCHEMI Toolkit 不仅能扩展单个模型和内核,还能为研究人员和开发者提供模块化的 PyTorch 原生结构,以构建自定义仿真工作流。
图 1 显示了此初始版本的 ALCHEMI Toolkit 中支持的 ALCHEMI 架构堆栈和产品功能,包括 Toolkit-Ops 中的扩展功能。此版本包括几何松和分子动力学功能,以及用于组合多个仿真工作流的支持工作流基础设施。
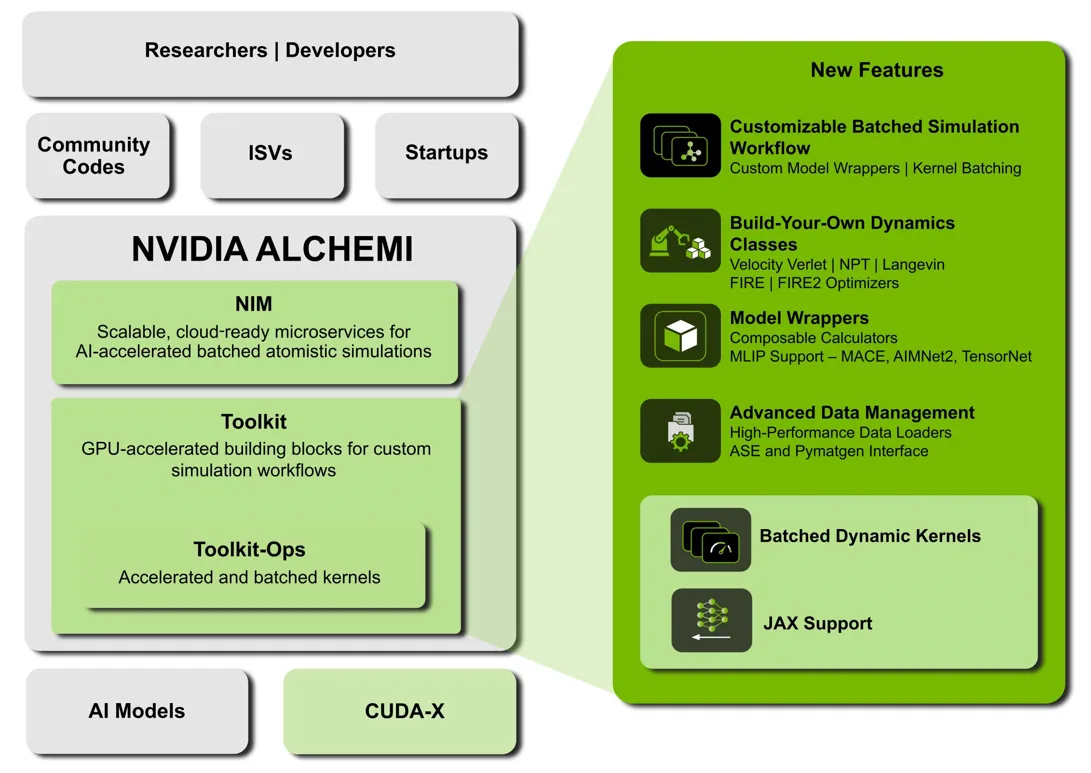
ALCHEMI 工具包如何推进数字化学的发展?
ALCHEMI 工具包不仅仅是脚本的集合。它旨在使研究人员和开发者能够轻松构建自定义的高性能原子模拟工作流程。
扩展 ALCHEMI 工具包 – Ops
ALCHEMI Toolkit 利用 Toolkit-Ops 的功能来处理模拟的基础计算。上一个版本包含几个关键运算:
- 近邻列表结构
- DFT-D3 色散校正
- 远距离静电相互作用
此版本扩展了常见操作的范围,包括:
- 批处理动态内核
- JAX 支持 (适用于 v0.2.0 版本功能)
与原子模拟生态系统集成
ALCHEMI 工具包旨在与更广泛的原子模拟生态系统无缝集成。我们很高兴地宣布,我们将与化学和材料科学领域的领先平台进行以下集成。
轨道
Orbital 开发了先进的 AI 基础模型,用于加速发现适用于数据中心和可持续材料的新型冷却系统。Orbital 已将 ALCHEMI Toolkit 集成到其新的 OrbMolv2 模型中,以大幅缩短推理所需的时间。新模型将利用 ALCHEMI Toolkit 组件,例如用于定期库伦相互作用的 PME 静电和用于批量恒定压力分子动力学的 MTK 积分器。现有的 Orb 模型已经利用 Toolkit-Ops 进行 GPU 加速的图形构建,在 TorchSim 支持下,可为大型系统提供约 1.7 倍的加速,为批量较小的系统提供约 33 倍的加速。
材质图形库 (MatGL)
MatGL 是一个开源框架,适用于基于图形的先进 MLIP。ALCHEMI 工具包与 MatGL TensorNet 模型集成,可显著加速材料模拟和属性预测工作流程。通过利用 ALCHEMI Toolkit GPU 原生内核和批处理基础设施,MatGL 用户可以在大规模模拟中实现更高的计算效率和更低的内存消耗。
Matlantis
Matlantis 通过将通用 MLIP 与高性能云计算相结合,实现快速的材料发现。Matlantis 正在积极探索 ALCHEMI 工具包,并确定其可组合动力学如何为工业材料模拟客户提供最大价值。这基于其经过验证的 ALCHEMI Toolkit-Ops 集成 (包括 Warp 优化的近邻列表构建和 DFT-D3 色散校正) ,可显著减少原子交互的计算开销,速度提升高达 10 倍。
此外,通过评估 ALCHEMI Toolkit 中的特定组件,这项合作有可能使 Matlantis 能够超越单一结构优化,实现数百万分子配置的高吞吐量、并行松。最终,这种集成旨在进一步推动小规模研究和工业规模的材料设计,以无与伦比的 GPU 效率加速化学评估。
如何开始使用 ALCHEMI 工具包
本节将为您介绍如何开始使用 ALCHEMI 工具包,该工具包简单易用。
系统和软件包要求
- Python* 3.11、* 3.14
- PyTorch@ 2.8
- CUDA 工具包 12+,NVIDIA 驱动 470.57.02+
- 操作系统:Linux (主要) 、macOS
- NVIDIA GPU ( RTX 20xx 或更高版本) ,CUDA 计算能力 = 7.0
- 最低 4 GB RAM (对于大型系统,建议使用 16 GB)
安装
使用以下代码安装 ALCHEMI Toolkit:
# Install Atomic Simulation Environment (ASE, used in the examples below)uv pip install ase# Using pippip install nvalchemi-toolkit# Using uvuv venv --seed --python 3.12uv pip install nvalchemi-toolkit# Install from sourcecd nvalchemi-toolkituv sync --all-extras# Add nvalchemi as a project dependencyuv add nvalchemi-toolkit |
有关更多信息,请参阅 NVIDIA/nvalchemi-toolkit GitHub 存储库和 ALCHEMI 工具包文档。
用于构建端到端工作流的 ALCHEMI Toolkit 的主要特性
本节将深入探讨 ALCHEMI Toolkit 的四个核心功能:可定制的批量仿真工作流、构建您自己的动态类、模型包装器和高级数据管理。这些功能为研究人员和开发者提供了创建定制端到端工作流所需的工具和灵活性,从而更大限度地提高 NVIDIA GPU 的效率和性能。
可定制的批量模拟工作流程
NVIDIA ALCHEMI 工具包的显著特点是 GPU 原生批量动态引擎。没有哪种 MLIP 模型能够完美适用于每种化学环境,尤其是在处理非局部、远程相互作用时。
ALCHEMI 工具包使研究人员能够将模块化化学和材料科学领域特定的内核和模型整合到定制的仿真工作流中。该架构支持开发专门的计算工作流,并运行具有数百万并发原子交互的虚拟实验室,而不会像传统软件堆栈那样延迟。
功能
- 将 MLIP 与基于物理性质的校正相结合的可组合计算器
- 高性能封装器 ( MACE、TensorNet、AIMNet2)
API 示例
以下示例构建数据、设置 MLIP 并配置 FIRE2 几何优化,然后将其用作 velocity Verlet (微规范) 动力学的起点:
from ase import Atomsfrom nvalchemi.data import AtomicData, AtomicBatchfrom nvalchemi.dynamics import ConvergenceHookfrom nvalchemi.dynamics.optimizers import FIRE2from nvalchemi.dynamics.integrator import VelocityVerlet# setup some batch of atomic structuresatomic_data = [AtomicData.from_atoms(Atoms(...), device="cuda") for _ in range(16)]batch = Batch.from_data_list(atomic_data)# setup your MLIP and dynamics classesmlip = ...# optimizer convergence depends on the force norm and max valuesconv_criteria = ConvergenceHook( criteria=[ {"key": "forces", "threshold": 0.05, "reduce_op": "norm"}, {"key": "forces", "threshold": 0.1, "reduce_op": "max"} ])optimizer = FIRE2( mlip, convergence_hook=conv_criteria, n_steps=200)velverlet = VelocityVerlet(mlip, n_steps=1000) |
您可以通过以下两种方式之一运行和扩展仿真流程:在单个 GPU 上,或在多个 CPU 和 GPU 上。
在单个 GPU 上运行和扩展工作流:FusedStage 类通过将两个或多个动态对象“添加”在一起而形成。这有助于在 torch.compile 中封装端到端工作流,并共享 CUDA 流上下文。
fused = optimizer + velverlet# context manager handles compilation and CUDA streamwith fused: # runs 200 steps of optimization and 1000 steps of MD fused.run(batch) |
通过这种方法,您可以轻松构建仿真工作流,在批量内的样本立即收时运行顺序步骤,并充分利用 GPU。
在多个 CPU 和 GPU 上运行和扩展工作流:第二种方法是在多个 CPU/ GPU 上分配工作流。然后,在两个动态类上使用管道运算符将 FIRE2 优化分配到一个 GPU 上,并在另一个 GPU 上分配 velocity Verlet 集成。
pipeline = optimizer | velverlet# equivalent to manual allocation with explicit producer/consumer# optimizer.next_rank = 1, velverlet.prior_rank = 0# DistributedPipeline({0: optimizer, 1: velverlet})with pipeline: pipeline.run(batch) |
虽然为了说明目的,我们特意简化了这个示例,但这种抽象允许用户将其工作流扩展到节点上的多个 GPU,并扩展到多个节点,以获得任意规模的数据集和秩数。
以下示例配置了 8 个 GPU 以运行几何优化,并通过管道传输结果在另外 8 个 GPU 上运行 Langevin 动力学:
from torch import distributed as distfrom torch.utils.data.distributed import DistributedSamplerfrom nvalchemi.data.datapipes import Dataset, DataLoader# set up distributed; torchrun --nproc-per-node 8 --nnodes 2 ...dist.initialize_process_group()# set up data and distributed samplerdataset = Dataset(...)data_sampler = DistributedSampler( dataset, num_replicas=dist.get_world_size(), rank=dist.get_rank())loader = DataLoader( dataset, batch_size=128, sampler=sampler, use_stream=True)# configure your pipeline; 8 ranks do optimization, 8 do langevin dynamicsoptimizers = [FIRE2(mlip, ..., next_rank=index + 8) for index in range(8)]dynamics = [Langevin(mlip, ..., prior_rank=index) for index in range(8)]pipeline = DistributedPipeline( {index: stage for index, stage in enumerate(optimizers + dynamics)})with pipeline: for batch in loader: pipeline.run(batch) |
构建您自己的动态类
ALCHEMI 工具包提供模块化架构,用于从头开始构建和自定义动态类。这种方法使社区能够将新的采样方法或热力学集成集成到 ALCHEMI 环境中,同时保持对底层内核的直接访问。这将动态转换为完全可定制的环境,用户可以在其中从头开始构建专门的动态类。
功能
- 专用的 GPU 优先轨迹分析工具
- 集成和可定制的动态内核 ( Velocity Verlet、NPT、Langevin 自动调温器)
- FIRE 和 FIRE2 优化器
API 示例
from enum import Enumimport torchfrom nvalchemi.data import Batchfrom nvalchemi.dynamics.base import BaseDynamics, DynamicsStagefrom nvalchemi.hooks import Hook, HookContextclass MySimulatedAnnealer(Hook): def __init__( self, t_start: float, t_end: float, cooldown_steps: int, frequency: int, stage: DynamicsStage ) -> None: # this hook will fire off every `frequency` MD steps, # bringing the temperature from `t_start` to `t_end` self.frequency = frequency self.t_start = t_start self.t_end = t_end self.cooldown_steps = cooldown_steps self.stage = DynamicsStage.BEFORE_STEP self.decay = (t_end / t_start) ** (1.0 / cooldown_steps) self._current_temp = t_start def __call__(self, ctx: HookContext, stage: Enum) -> None: # access the calling dynamics class through `HookContext` dynamics = ctx.workflow dynamics.target_temperature = max( dynamics.target_temperature * self.decay, self.t_end )class VelocityVerlet(BaseDynamics) __needs_keys__: {"energies", "forces", "masses", "velocities"} __provides_keys__: {"positions"} def __init__( self, model: BaseModelMixin, n_steps: int, dt: float = 1.0, # timestep target_temperature: float = 300.0, # initial temperature tau: float = 10.0, # coupling constant hooks: list[Hook] | None = None, convergence_hook: ConvergenceHook | dict | None = None, **kwargs, ): super().__init__(model=model, n_steps=n_steps, hooks=hooks, convergence_hook=convergence_hook) self.dt = dt self.target_temperature = target_temperature self.tau = tau self._prev_accelerations = None def pre_update(self, batch: Batch) -> None: # perform the first half of velocity Verlet with torch.no_grad(): accelerations = batch.forces / batch.masses self._prev_accelerations = accelerations.clone() batch.positions.add_( batch.velocities * dt + 0.5 * accelerations * dt**2.0 ) def post_update(self, batch: Batch) -> None: # perform second half of velocity Verlet, with thermostat # temperature update with torch.no_grad(): new_accelerations = batch.forces / batch.masses batch.velocities.add_(0.5 * (self._prev_accelerations + new_accelerations) * self.dt) ke_per_atom = 0.5 * batch.masses * (batch.velocities**2).sum(dim=-1, keepdim=True) # get the total kinetic energy per system total_ke = scatter_add_(...) current_temp = 2.0 * total_ke / (batch.num_atoms * 3.0) ratio = self.target_temperature / current_temp lam = torch.sqrt( torch.tensor(1.0 + (self.dt / self.tau) * (ratio - 1.0)) ).clamp(min=0.8, max=1.2) # clamp for stability batch.velocities.mul_(lam)# configure the new dynamics classmy_velverlet = VelocityVerlet( ..., hooks=[ MySimulatedAnnealer(t_start=900.0, t_end=300.0, cooldown_steps=10, frequency=100, stage=DynamicsStage.BEFORE_STEP) ],) |
模型包装器
借助 ALCHEMI 工具包,您可以使用自己的预训练模型和加速物理组件。它为将您自己的模型导入管道提供了必要的基础架构,确保专有架构或特定领域的架构能够利用 GPU 原生编排。这抽象化了不同模型类型的复杂性,提供了从独立模型到生产就绪型高吞吐量仿真的标准化路径。
功能
- MLIP 支持 ( MACE、TensorNet、AIMNet2)
- 可组合计算器
- 标准化模型配置
API 示例
from beartype import beartypefrom super_mlip import BestMLIPModelfrom nvalchemi._typing import ModelOutputsfrom nvalchemi.models.base import BaseModelMixin, ModelConfig, NeighborConfigclass BestMLIPWrapper(nn.Module, BaseModelMixin): def __init__(self, model: BestMLIPModel, **kwargs): super().__init__(**kwargs) # ModelConfig declares model capabilities (which are frozen) # and runtime control (mutable) for the rest of the framework self.model_config = ModelConfig( outputs=frozenset({"energy", "forces", "hessians"}), # this is actually the default value required_inputs=frozenset({"positions", "atomic_numbers"}) autograd_outputs=frozenset({"forces"}), neighbor_config=NeighborConfig(cutoff=5.0, format="coo")) def adapt_input(self, data: Batch, **kwargs) -> dict[str, Any]: # adapts the nvalchemi data structure to what is # expected by the model model_inputs = super().adapt_input(data, **kwargs) # dict structure expected by BestMLIPModel model_inputs["atom_numbers"] = data.atomic_numbers model_inputs["coords"] = data.positions return model_inputs def adapt_output(self, model_output: any, data: Batch) -> ModelOutputs: # adapt the model outputs from the model's forward pass to # format expected by nvalchemi output = super().adapt_output(model_output, data) energies = model_output["energies"] output["energies"] = energies # check model config for expected outputs if "forces" in self.model_config.active_outputs: output["forces"] = model_output["forces"] return output # beartype decorator is optional, but will runtime type check arguments @beartype def forward(self, data: Batch, **kwargs) -> ModelOutputs: model_inputs = self.adapt_input(data, **kwargs) # calls BestMLIPModel's forward definition based on MRO model_outputs = super().forward(**model_inputs) return self.adapt_output(model_outputs, data) |
高级数据管理
传统上,在 CPU 和 GPU 之间移动数据的“内存税”是 AI 驱动的发现过程中的一个重大瓶颈。ALCHEMI Toolkit 可充当科学数据的专用编排器,提供构建自定义提取流程所需的基础架构,以便将信息从标准研究文件移动到优化的 GPU 张量中。
这支持扩展发现,使工业规模的模拟能够通过熟悉的界面进行访问。通过标准化原子信息的表示和加载方式,ALCHEMI Toolkit 可确保数据始终驻留在设备上,这意味着整个模拟都保留在 GPU 上,从而实现批量模拟,以优化 GPU 利用率并消除通信开销。
功能
- 高性能数据加载器
- ASE 和 Pymatgen 接口
- AtomicData 和批处理对象
API 示例
from nvalchemi import AtomicData, Batchfrom nvalchemi import datafrom ase.build import slabatoms = slab(...)# Create AtomicData object from ase.Atoms objectdata = AtomicData.from_atoms(atoms, device="cuda")>>> data ...data.node_propertiesdata.system_properties# Create a Batch object from a list of AtomicDatabatch = Batch.from_data_list([data, data, data])batch.num_graphsbatch.get_data(0)# get first three samplesbatch[:2]batch[mask]batch["energies"] -> ...batch.from_atoms([ase.Atoms,...])# Create a dataset from ase.Atomswriter = data.AtomicDataZarrWriter("atom_dataset.zarr")# writer will amortize overhead by writing batches of data;# this is equivalent to writing individual samples but efficientlywriter.write(batch)# Read the data from zarrreader = data.AtomicDataZarrReader("atom_dataset.zarr")# Dataset treats device natively; individual samples # are placed on GPU and it accelerates preprocessing transforms;# num_workers sets the number of threads used for async prefetchingdataset = data.Dataset(reader, device = "cuda", num_workers=4)dataloader = data.DataLoader(dataset, batch_size=16)for batch in dataloader: # do something with batch |
开始使用 ALCHEMI 工具包构建分子工作流程
ALCHEMI 工具包为研究人员和开发者提供构建端到端 GPU 原生分子工作流所需的低级基元和高级抽象。将关键瓶颈 (例如近邻列表构建、结构松和集成步骤) 转移到 PyTorch 生态系统中,可以消除主机到设备的内存传输开销,而这种开销传统上限制了 MLIP 驱动的模拟。
无论您是合成混合 ML 或物理势,还是扩展批量分子动力学,ALCHEMI Toolkit 都可提供必要的 API Hook,以便在不牺牲性能的情况下管理复杂的张量状态。
要加速化学和材料科学模拟,并探索构建您自己的自定义工作流,请访问 NVIDIA/nvalchemi-toolkit GitHub 资源库和 ALCHEMI Toolkit 文档。在继续扩展受支持的操作和架构库的同时,我们鼓励您克隆存储库,探索所提供的 Jupyter Notebook,并开始将这些 GPU 加速的工作流集成到您自己的发现流程中。
致谢
我们在此感谢 Orbital 的 James Gin、Tim Duignan、Vaidas imkus、MatGL 的 Shyue Ping Ong 教授、Matlantis 的 Susumu Rhino、Ryuhei Okuno 和 Jethro Tan 与我们合作,将 NVIDIA ALCHEMI Toolkit 应用到他们的平台中。我们还要感谢 Nikita Fedik、Roman Zubadyuk、Atul Thakur 和 Logan Ward 对此博文的贡献。
